2 estructura y replicacion del dna 1 (1)
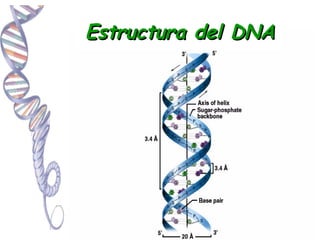
- 3. Estructura del DNA Adenina se aparea con Timina Guanina se aparea con Citosina
- 4. Implicaciones del Diámetro constante
- 6. Bases Físicas de la Herencia Procariotes HU y H Eucariotes • Histonas • No histonas
- 9. Bases Físicas de la Herencia
- 10. Table 12-2 Copyright © 2006 Pearson Prentice Hall, Inc.
- 11. Bases Físicas de la Herencia
- 12. Bases Físicas de la Herencia
- 13. Bases Físicas de la Herencia
- 14. Bases Físicas de la Herencia
- 15. Bases Físicas de la Herencia
- 16. Bases Físicas de la Herencia
- 17. Bases Físicas de la Herencia
- 18. Bases Físicas de la Herencia Eucromatina Cromatina Constitutiva Heterocromatina Facultativa
- 19. Bases Físicas de la Herencia DNA Centrómeros Flia alfoide Altamente 170 pb-106 pb Repetitivo 5% Telómeros Tandem DNA Sec dispersas SINE Moderadam. LINE Repetitivo 30% RNAr Sec repetidas VNTR STR
- 25. Cumple el DNA las condiciones del material hereditario? Condiciones Componente del DNA Tiene información biológica Código Genético: 3 bases para las proteínas codifican para 1 aminoácido (proteína) Replicarse fielmente y Las bases complementarias transmitirse a la son fieles; se encuentran en descendencia las células germinales Debe ser estable en un Uniones covalentes; puentes organismo vivo de hidrógeno Capaz de incorporar cambios Las bases pueden cambiar estables por mecanismos conocidos
- 26. Replicación del DNA La Replicación del DNA es simple, pero requiere un gran grupo de enzimas y proteínas: La Helicasa desenrolla la molécula Las proteínas de unión a cadena sencilla estabilizan el ssDNA La Primasa inicia la replicación con RNA La DNA polimerasa extiende el nuevo DNA La segunda DNA polimerasa remueve el RNA La DNA ligasa une todos los fragmentos
- 29. Replicación del DNA •Enzimas que sintetizan (replican) el DNA •E. coli •DNA polimerasa I (rellena huecos y repara) •DNA polimerasa II y III (función principal en la síntesis) •Añade bases en ambas cadenas en la dirección 5’ → 3’ •Requiere un 3’ OH final •Eucariotes •5 polimerasas ∀α y β principal en replicación ∀δ, ε y γ exonucleasas •Corrección de pruebas: actividad 3’ → 5’ exonucleotídica. Sustituye bases mal emparejadas por correctas
- 31. Acción Autocatalítica del DNA
- 32. Proteínas principales replicación • Topoisomerasas: rompen una hebra y la tensión del enrrollamiento de la hélice se relaja • Helicasas: completan el desenrrollamiento • ADN polimerasas: complejos agregados de diferentes proteínas. • Primasas: sintetizan los iniciadores de ARN que se necesitan para iniciar la replicación • Ligasas: sellan las lagunas dejadas por las ribonucleasas cuando remueven los primers, catalizan la unión fosfodiester entre nucleótidos adyacentes. • Proteinas de unión a la hebra sencilla del ADN: estabilizan la horquilla de replicación.
- 35. Replicación del DNA •Replicación: continua (cadena adelantada) y discontinua (cadena retrasada) •Discontinua •Cebador (pequeño RNA 2-60 nucleótidos añadido por la primasa o RNA pol que provee 3’ OH) •Fragmento de Okazaki por DNA pol III (1500 bp en procariotas y 150 en eucariotas) •Pol I elimina cebador 3’ -> 5’ y llena huecos (gap) •Ligación (DNA ligasa, enlace fosfodiéster)
- 39. Existen las dos formas de replicación: En general, es Bidireccional: • genomas bacterianos • cromosomas de células eucariotas En algunos casos es Unidireccional, ej: • en el ADN mitocondrial • en algunos virus
- 46. Replicación del DNA •Enzimas que sintetizan (replican) el DNA •E. coli •DNA polimerasa I (rellena huecos y repara) •DNA polimerasa II y III (función principal en la síntesis) •Añade bases en ambas cadenas en la dirección 5’ → 3’ •Requiere un 3’ OH final •Eucariotes •5 polimerasas ∀α y β principal en replicación ∀δ, ε y γ exonucleasas •Corrección de pruebas: actividad 3’ → 5’ exonucleotídica. Sustituye bases mal emparejadas por correctas
- 48. Telomerasa • Ribonucleoproteína específica de los telómeros • Tiene actividad transcriptasa reversa • Añade unidades sencillas de la repetición a los extremos de los telómeros previniendo el acortamiento de los cromosomas • Contiene un molde de ARN que sirve para sintetizar el ADN y la subunidad catalítica que actúa como transcriptasa reversa. • Las mayoría de las células somáticas normales del ser humano son TELOMERASA-NEGATIVAS
- 49. • Se ha detectado actividad telomerasa en: 1. Células hematopoyéticas: estimulación de los linfocitos T con algún mitógeno eleva los niveles de telomerasa 500-1000 veces. 2. Queratinocitos basales 3. Células epiteliales del endometrio, mamas, esófago, próstata y páncreas. • La actividad telomerasa es mayor en mujeres con ciclo menstrual activo y es casi nula en la menopausia • El epitelio lobular de las mamas tiene más actividad telomerasa durante el embarazo • La actividad telomerasa baja cuando las células se especializan y dejan de dividirse.
- 54. TRANSCRIPCION • El proceso mediante el cual la información almacenada en el DNA se recupera mediante la síntesis de RNA dependiente de un molde.
- 55. REPLICACION Y TRANSCRIPCION SIMILITUDES • Se utilizan nucleótidos trifosfatados • El crecimiento de la cadena va en dirección 5’3’ DIFERENCIAS • Solo se transcribe una hebra de DNA • Solo una pequeña fracción del genoma es transcito
- 56. RNA (Acido Ribonucleico) • Tipos mas importantes: – mRNA Se sintetiza a partir de DNA y se utiliza como molde para la síntesis proteica en ribosomas – rRNA Compone los ribosomas que se encargan de la síntesis de proteínas – tRNA Se une a los aminoácidos y los transporta al ribosoma para la síntesis de proteínas
- 57. RNA POLIMERASA • Es la enzima que cataliza el proceso de trascripción: Mg2+ DNA n(ATP+CTP+GTP+UTP) ═ (AMP-CMP-GMP-UMP)n + nPPi • El producto de la rxn es una copia complementaria del DNA molde
- 58. RNA POLIMERASA • En procariotes una sola RNA pol cataliza la síntesis de las tres clases de RNA • La RNA pol cataliza la reacción de transcripción a una velocidad aprox. 50 nucleótidos/s • En E. coli hay aprox. 3000 moléculas de RNA pol • Una vez la RNA pol se une a un molde de DNA e inicia la transcripción rara vez se disocia hasta que llega a una señal de terminación
- 59. RNA POLIMERASA
- 60. MECANISMO DE LA TRANSCRIPCION • INICIACION Interacción con los promotores • ELONGACION Incorporación de los ribonucleótidos • TERMINACION Finalización de la trascripción dependiente o independiente del factor
- 61. La Estructura del RNA
- 62. Transcripción • Se abre una pequeña sección de DNA • Solo se usa una de las hebras de DNA para la transcripción (3’ - 5’). • Esta sirve de molde para formar el mRNA • El mRNA se sintetiza de nucleótidos libres en la célula
- 63. Figure 13-9 Copyright © 2006 Pearson Prentice Hall, Inc.
- 64. Figure 13-9a Copyright © 2006 Pearson Prentice Hall, Inc.
- 65. Figure 13-9b Copyright © 2006 Pearson Prentice Hall, Inc.
- 66. Figure 13-9c Copyright © 2006 Pearson Prentice Hall, Inc.
- 68. Transcripción • E. coli: TTGACA (–35) y TATAAT (–10). •Terminación directa debida a la formacion de bucle the RNA. •In some cases, termination depends on the rho (ρ) termination factor
- 69. TERMINACION INDEPENDIENTE DEL FACTOR
- 70. TERMINACION DEPENDIENTE DEL FACTOR
- 71. DIFERENCIAS IMPORTANTES ENTRE PROCARIOTES Y EUCARIOTES PROCARIOTES EUCARIOTES Todo el DNA contenido en una Genoma dividido en varios o única molécula muchos cromosomas (1-190) El cromosoma bacteriano se Los cromosomas se encuentra libre en el citosol encuentran dentro del núcleo formando la cromatina (DNA- proteína) Haploides (una sola copia del Mayoría diploides (dos copias material genético) de un cromosoma) Transcripción y traducción Transcripción dentro del núcleo acopladas y traducción en el citoplasma No tienen intrones Intrones y exones
- 72. Que son los genes Los genes son secuencias de nucleótidos que codifican información para crear proteínas. Su tamaño varia desde menos de 100 pares de bases hasta varios millones de pares de bases.
- 73. • Todos los organismos eucariotes (organismo con células nucleadas, contrario a las bacterias que no poseen núcleo y se llaman procariotes) poseen genes que están divididos en exones e intrones. El significado biológico de esta segmentación no se conoce claramente. • La mayoría de los genes humanos están divididos en exones e intrones, excepto los genes mitocondriales y algunos genes del núcleo. • Durante la expresión génica tanto los exones como los intrones son transcritos para formar el pre- ARNm.
- 74. • El proceso de “splicing” del ARN elimina los intrones y produce una molécula de ARNm madura que codifica por un polipéptido. • Los exones se definen como secuencias que están representadas en el ARNm maduro. • Estos pueden o no codificar una proteína: algunos exones localizados en los extremos 3’ y 5’ del ARNm pueden no ser traducidos a proteínas.
- 75. Estructura del gen eucariotico • Exón: secuencia codificante • Intrón: secuencia no codificante entre dos exones
- 76. TRANSCRIPCION EN EUCARIOTAS • Es un proceso de mucha discriminación (según el tejido o etapa del desarrollo serán los genes que se van a transcribir) • La maquinaria de la transcripción debe tener en cuenta la compleja estructura de la cromatina eucariota • Requiere de varios tipos de RNA polimerasas • La RNA polimerasa requiere de factores adicionales llamados factores de transcripción para iniciar la transcripción • Tiene que haber un procesamiento complejo del mRNA que permita escindir los intrones del mensaje y transportar la molécula al citoplasma
- 77. Figure 13-10 Copyright © 2006 Pearson Prentice Hall, Inc.
- 78. RNA POLIMERASAS POLIMERASA LOCALIZACION RNA SINTETIZADOS I Núcleo pre – rRNA (excepto la subunidad 5S) II Núcleo pre – mRNA, RNA nucleares pequeños (snRNA) III Núcleo pre – tRNA, rRNA 5S, otros snRNA Mitocondrial Mitocondria Mitocondrial Cloroplástica Cloroplasto Cloroplástico
- 79. RNA POLIMERA III • TRANSCRIBE LOS PRINCIPALES GENES DE RNA DE TRANSFERENCIA, RNA RIBOSOMAL 5S Y RNA PEQUEÑOS • Contiene 14 subunidades • Requiere varios tipos de factores de transcripción como TFIIIA, TFIIIB y TFIIIC
- 80. RNA POLIMERASA I • TRANSCRIBE LOS PRINCIPALES GENES DE RNA RIBOSOMICO • Contiene 13 subunidades • Necesita al menos 2 factores de transcripción para iniciar el proceso • El ribosoma eucariota contiene 4 moleculas de rRNA – Subunidad pequeña: 18S – Subunidad grande: 28S, 5.8S y 5S (no transcrito por esta RNApol)
- 81. RNA POLIMERASA II • TRANCRIBE LOS GENES ESTRUCTURALES, ES DECIR, LOS QUE SE TRADUCEN A PROTEINAS • Contiene múltiples subunidades • Intervienen al menos 7 factores de transcripción: TFIIA, TFIIB, TFIID, TFIIE, TFIIF, TFIIH y TFIIJ • El factor critico es TFIID que se une a la caja TATA que es el equivalente eucariota a la región -10
- 82. FACTOR DE FUNCION TRANSCRIPCION TFIID Reconoce la caja TATA TFIIA Estabiliza el complejo entre TFIID y el DNA TFIIB Recluta a la RNApol II y TFIIF TFIIF Ayuda a que la pol II reconozca el promotor RNA pol II Cataliza la síntesis de RNA, recluta a TFIIE TFIIE Recluta a TFIIH y regula la actividad helicasa de TFIIH TFIIH Desenrolla la región promotora
- 83. Transcripción •
- 88. FORMACION COMPLEJO TRANSCRIPCION RNA pol II •La caja TATA se une al factor de transcripción TFIID, determina el sitio de inicio (aprox 10 subunidades) •Incluye una prot de union a TATA (TBP) se une especificamente a TATA y a otros factores asociados a TBP (TAFs) •El TBP se une a un segundo factor transcripcional (TFIIB) formando complejo TBP – TFIIB en el promotor.
- 89. • EL TFIIB sirve de puente para que la RNA pol II se una al complejo TBP – TFIIB en asociacion con un tercer factor TFIIF. • Luego se requiere la union de dos factores adicionales para iniciar la transcripción: TFIIE, TFIIH. • TFIIH multisubunidad: 2 subunidades tienen funcion helicasa, otra subunudad tiene funcion quinasa •
- 90. • Potenciadores: rio arriba, dentro o rio abajo del gen y modulan la transcripción • Terminacion • hnRNA es procesado: 5' cap, poli-A y splicing
- 91. Transcripción
- 92. Transcripción Tipos de RNA • mRNA (mensajero) • tRNA (transferencia) • rRNA (ribosomal) • miRNA (micro RNA)
- 93. mRNA • Cadenas de largo tamaño con estructura primaria. • Se llama mensajero porque transporta la información para síntesis proteica. • La información de cada mRNA sintetiza una proteína determinada. • Su vida media es corta.
- 94. mRNA • Contiene codones (grupo de 3 nucleótidos que codifica para un a.a. en la cadena de polipéptidos). Señala el comienzo y el final de la cadena polipéptida. • En procariotas el extremo 5’ posee un grupo trifosfato • En eucariotas el extremo 5’ posee un grupo metil-guanosina (cap) unido al trifosfato, y el extremo 3´posee una cola de poli-A
- 95. tRNA • Tiene forma de hoja de trébol • Tiene una cola C-C-A 3’, donde se pega el A.A. • Contiene el anticodón (grupos de 3 nucleótidos complementarios al codón.) • Su misión es unirse a un aminoácidos y transportarlo hasta el ARNm para sintetizar proteínas.
- 96. tRNA
- 97. rRNA • Es más estable. • Se divide en sub- unidades
- 98. Propiedades del código genético • Unidireccional – lee 5’ - 3’ • No es superponible - codón independiente, (lee de tres en tres) • Colineal – la secuencia de a.a. corresponde a una ubicación de la secuencia de cada tres nucleótidos. • Redundante – la mayoría de los a.a. pueden ser codificados por varios codones.
- 99. Propiedades del código genético • Universal – el mismo código se cumple para todos los seres vivos. • Señal iniciadora – AUG corresponde a formil-metionina. • Señal de terminación – UAA, UAG, UGA, tripletes sin sentido.
- 101. Síntesis de proteínas • Transcripción • Traducción Iniciación Elongación Terminación
- 102. Traducción: (iniciación) • Envuelve la unión entre el tRNA con el primer codón del mRNA. • El primer codón es AUG (metionina) • El primer tRNA que llega se coloca en el lugar P (peptidil) del ribosoma.
- 104. INICIACION EN EUCARIOTES • El eIF1, y eIF3: Subunidad 40 s • eIF2 (GTP): RNAT met a la sub 40s • La cap 5’ reconocida eIF4F, eIF4A, eIF4B acoplan RNAm y ribosoma • La sub 40s + RNAT met y el eIF5 dirigen mensajero para identificar AUG de inicio • Al ser reconocido el eIF5 produce hidrólisis de GTP, los IF salen y sub 60s (eIF6) se une a 40s
- 105. Traducción: (elongación) • Formación de la cadena de a.a. para formar la proteína • Llega el segundo tRNA cargado y se coloca en el lugar A (aceptador) para formar el enlace péptidico, mediante la enzima peptidyltransferasa, esto se conoce como transpeptidación.
- 106. Traducción: (elongación) • La translocación se lleva a cabo cuando el primer tRNA (met) se mueve del lugar P al lugar E (“exit”). • El tRNA que estaba en el lugar A se mueve al P • El mRNA se mueve al siguiente codón para ser reconocido por el tRNA en el lugar A.
- 107. ELONGACION EUCARIOTES • eEF1α (GTP) = EF-Tu de bacterias • eEF2 (GTP) = EF- G de bacterias • eEF1β (GTP) recicla (GTP) eEF1α
- 109. Traducción: (terminación) • Luego de haberse formado la cadena de polipéptidos (elongación), se va colocar un codón de terminación (UAA, UAG, UGA) • Cuando el tRNA llega no reconoce el codón y detiene el proceso de elongación y se termina con la síntesis de proteína
- 110. TERMINACION EN EUCARIOTES • Solo un factor de liberación (RF) • 10 millones ribosomas /célula • 18 residuos de aa/ seg (20 aa diferentes) • DNA pol 10 N/seg. • RNA pol 55 N/seg • Síntesis proteínas 200M/ enlaces/ seg
- 112. 1865 Beadle & Tatum - 1941 La hipótesis un gen – una enzima ¿Cómo funciona el genoma para manifestar sus características? Gen 1 Gen 2 Gen 3 Producto Precursor Enz 1 A Enz 2 B Enz 3 final
- 113. 1865 Beadle & Tatum - 1941 La hipótesis un gen – una enzima Neurospora crassa
- 114. Figure 14-11a Copyright © 2006 Pearson Prentice Hall, Inc.
- 115. Figure 14-11b Copyright © 2006 Pearson Prentice Hall, Inc.
- 116. Figure 14-11c Copyright © 2006 Pearson Prentice Hall, Inc.
- 117. Figure 14-11 Copyright © 2006 Pearson Prentice Hall, Inc.
- 118. 1865 Beadle & Tatum - 1941 La hipótesis un gen – una enzima Ascosporas en medio completo Neurospora crassa Rayos X Mínimo + Todos amino ácidos crecen medio mínimo No crecen los mutantes Mutantes deficientes en la síntesis de arginina. Cys Glu Arg Lys His
- 119. 1865 Beadle & Tatum - 1941 + Ornithine + Citruline Minimal + Arginine Medium Gene A Gene B Gene C Tipo Precursor Enz A Ornithine Enz B Citruline Enz C Arginine normal BLOQUEO Mutantes Precursor Ornithine Enz B Citruline Enz C Arginine clase I Mutantes clase II Precursor Enz A Ornithine Citruline Enz C Arginine Mutantes clase III Precursor Enz A Ornithine Enz B Citruline Arginine
- 120. Figure 14-10 Copyright © 2006 Pearson Prentice Hall, Inc.
Notes de l'éditeur
- Table 12-2 Categories and Properties of Histone Proteins
- Figure 13-9 The early stages of transcription in prokaryotes, showing (a) the components of the process; (b) template binding at the site involving the sigma subunit of RNA polymerase and subsequent initiation of RNA synthesis; and (c) chain elongation, after the sigma subunit has dissociated from the transcription complex and the enzyme moves along the DNA template.
- Figure 13-9a The early stages of transcription in prokaryotes, showing (a) the components of the process; (b) template binding at the site involving the sigma subunit of RNA polymerase and subsequent initiation of RNA synthesis; and (c) chain elongation, after the sigma subunit has dissociated from the transcription complex and the enzyme moves along the DNA template.
- Figure 13-9b The early stages of transcription in prokaryotes, showing (a) the components of the process; (b) template binding at the site involving the sigma subunit of RNA polymerase and subsequent initiation of RNA synthesis; and (c) chain elongation, after the sigma subunit has dissociated from the transcription complex and the enzyme moves along the DNA template.
- Figure 13-9c The early stages of transcription in prokaryotes, showing (a) the components of the process; (b) template binding at the site involving the sigma subunit of RNA polymerase and subsequent initiation of RNA synthesis; and (c) chain elongation, after the sigma subunit has dissociated from the transcription complex and the enzyme moves along the DNA template.
- Figure 13-10 Posttranscriptional RNA processing in eukaryotes. Heterogeneous nuclear RNA (hnRNA) is converted to messenger (mRNA), which contains a cap and a -poly-A tail, which then has introns spliced out.
- Figure 14-11a Induction, isolation, and characterization of a nutritional auxotrophic mutation in Neurospora. In (a), most conidia are not affected, but one conidium (shown in red) contains such a mutation. In (b) and (c), the precise nature of the mutation is determined to involve the biosynthesis of tyrosine.
- Figure 14-11b Induction, isolation, and characterization of a nutritional auxotrophic mutation in Neurospora. In (a), most conidia are not affected, but one conidium (shown in red) contains such a mutation. In (b) and (c), the precise nature of the mutation is determined to involve the biosynthesis of tyrosine.
- Figure 14-11c Induction, isolation, and characterization of a nutritional auxotrophic mutation in Neurospora. In (a), most conidia are not affected, but one conidium (shown in red) contains such a mutation. In (b) and (c), the precise nature of the mutation is determined to involve the biosynthesis of tyrosine.
- Figure 14-11 Induction, isolation, and characterization of a nutritional auxotrophic mutation in Neurospora. In (a), most conidia are not affected, but one conidium (shown in red) contains such a mutation. In (b) and (c), the precise nature of the mutation is determined to involve the biosynthesis of tyrosine.
- Figure 14-10 Metabolic pathway involving phenylalanine and tyrosine. Various metabolic blocks resulting from mutations lead to the disorders phenylketonuria, alkaptonuria, albinism, and tyrosinemia.
