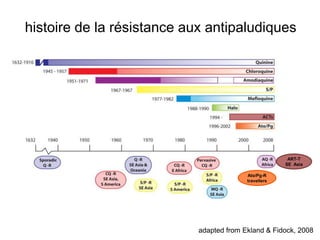
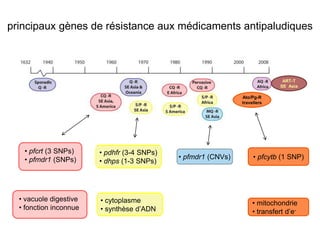
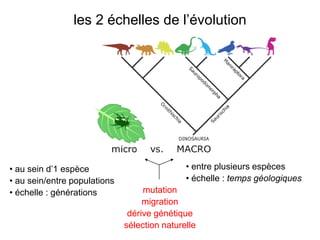
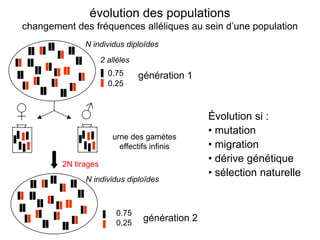
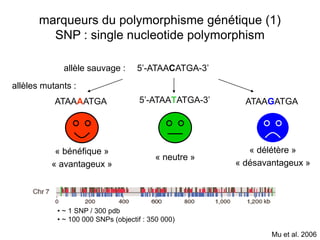
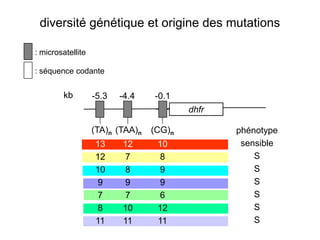
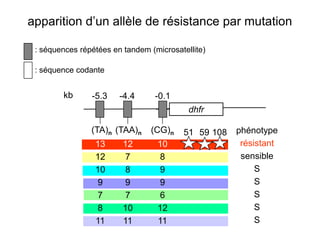
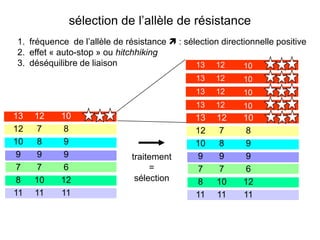
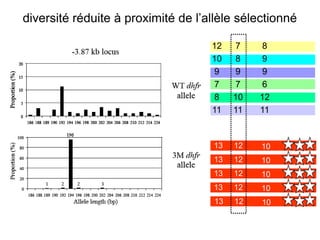
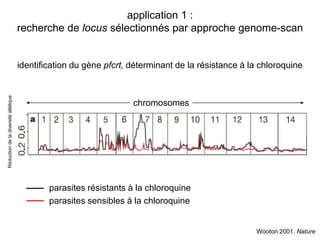
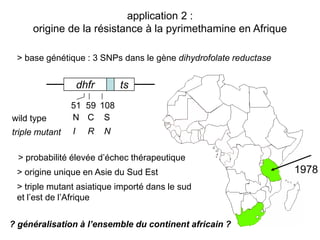
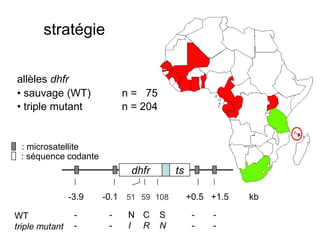
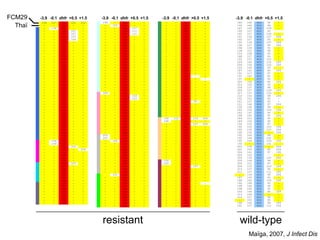
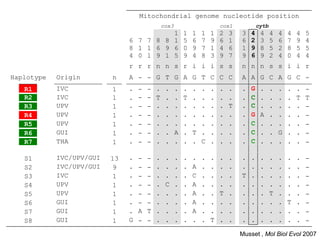
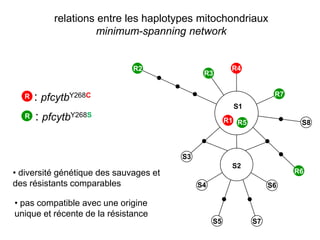
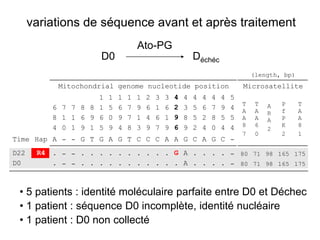
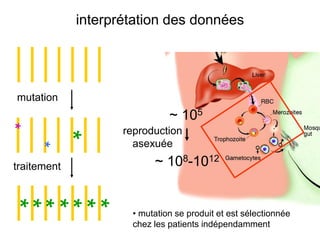
Le document traite de l'évolution de la résistance de Plasmodium falciparum aux médicaments antipaludiques, en mettant en lumière divers gènes de résistance et leurs mécanismes. Il explore également les origines de cette résistance, notamment la résistance à la pyriméthamine et à l'atovaquone-proguanil, ainsi que les implications de la sélection naturelle sur les allèles de résistance. Enfin, il souligne l'importance de l'analyse génétique pour comprendre la dynamique de la résistance aux traitements antipaludiques.