Zarski hépatites virales du16 jpz
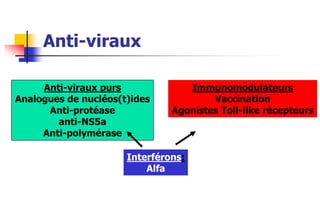
- 1. Anti-viraux Anti-viraux purs Analogues de nucléos(t)ides Anti-protéase anti-NS5a Anti-polymérase Immunomodulateurs Vaccination Agonistes Toll-like récepteurs Interférons: Alfa
- 3. Antiviraux Hépatite B Analogues de: Nucléosides Nucléotides Interféron a Nouvelles cibles Hépatite C Anti-protéases Anti-polymérase: NS5B Nucléosidiques Non nucléosidiques Anti-NS5a Ribavirine Interféron? Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 4. Antiviraux Hépatite B Interféron α Analogues de: Nucléosides Nucléotides Hépatite C Anti-protéases Anti-polymérase: Nucléosidiques Non nucléosidiques Ribavirine Interféron? Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 5. Organisation du génome VHC et maturation de la polyprotéine Asselah T et al. Liver International 2009;29(s1):57-67. C E1 E2 p7 NS2 NS3 4A NS4B NS5A NS5B NS2/3 protéase Host signal peptidase Host signal peptide peptidase NS3/4A protéase Serine protéase Hélicase CofacteurSeri ne protéase ARN-polymérase ARN-dépendanteProtéaseGlycoprotéines d’enveloppe Core Protéines structurales Protéines non-structurales Cadre de lecture TRADUCTION MATURATION 5’NCR 3’NCR NCR : Non Coding Region
- 6. Adapté de Lindenbach et al. Nature. 2005; 436(7053): 933-8. Cibles des antiviraux directs (DAAs) Liaison au récepteur et endocytose Transport et relargage Réplication ARN Assemblage des virions Traduction et formation de la polyprotéine Inhibition de la réplication Inhibition de l’assemblage Fusion et décapsidation ARN (+) Inhibition de la maturation de la polyprotéine
- 7. Les anti-viraux directs I protéase Anti-NS5a I polymérase nucléotidique I Polymérase non nucléotidique Giléad GS-9451 GS-9857 Ledipasvir Velpatasvir Sofosbuvir GS-9669 Abbvie Paritaprévir/r Ombitasvir ABT-530 Dasabuvir Merck (MSD) Grazoprévir Elbasvir MK-8408 Samatasvir MK-3682 IDX-459 MK-8876 BMS Asunaprévir Daclatasvir Béclabuvir Janssen (J&J) Siméprévir GSK-2336805 TMC-055/r Achillion Sovaprévir ACH-3102 ACH-3422
- 8. Adapté de Lindenbach et al. Nature. 2005; 436(7053): 933-8. Antiprotéases (anti-NS3/4A) Liaison au récepteur et endocytose Transport et relargage Réplication ARN Assemblage des virions Traduction et formation de la polyprotéine Fusion et décapsidation ARN (+) Inhibition de la maturation de la polyprotéine
- 9. Saalau-Bethell et al. Nat Chem Biol. 2012; 8(11): 920-5. Mécanisme d’action des antiprotéases Substrat / inhibiteur de la protéase Partie C-terminale du domaine hélicase Linker flexible entre les domaines hélicase et protéase Conformation fermée (auto-inhibée) Conformation ouverte (active)
- 10. Anti-protéase Mécanismes Inhibe la sérine protéase NS3/NS4 responsable du développement de la poly-protéine et de la production de nouveaux virions G1a et 1b Faible barrière de résistance Effets II: anémie, prurit, dysgueusie, rash, photosensibilité, bilirubine Molécules Siméprévir (Olysio®, Janssen) Bocéprévir, Télaprévir Asunaprévir (BMS) Paritaprevir/r (Abbvie) Grazoprevir (MSD) Sovaprevir (Achillion) GS-9451 (Gilead) GS-9857 (Gilead)
- 12. Tellinghuisen et al. Nature. 2005; 435(7040): 374-9. Organisation de la protéine NS5A Domaine I Domaine II Domaine III 1977 2003 2189 2226 2314 2328 2442 Association membranaire Nécessaire pour la localisation des gouttelettes lipidiques et l’assemblage viral Nécessaire pour la co-localisation avec la protéine Core sur les gouttelettes lipidiques et l’assemblage viral Interaction avec ApoE Interaction avec PI4K-IIIα
- 13. Nettles et al. J Med Chem. 2014; 57(23): 10031-43. Interaction des anti-NS5A avec NS5A Membrane du réticulum endoplasmique Cytosol Lumière Liaison à la protéine Core
- 14. Eyre et al. Gastroenterology. 2014; 147(5): 959-62. Sites d’action des inhibiteurs de NS5A Lumière du réticulum endoplasmique Inhibiteurs NS5A NS3-4A NS4B NS5A (dimère) NS5B PI4KIIIα PI4P Facteurs hôtes ARN VHC cholestérol Synthèse PI4P Stabilité NS5A Dimérisation NS5A Multimérisation NS5A Formation vésicule double membrane Mécanismes d’action des anti-NS5A
- 15. Inhibiteurs anti-NS5A Activité G1 & G4 et G3* Autres génotypes variables Faible barrière à la résistance Activité pangénotypique Plus forte barrière à la résistance (/1ère) 1ère génération 2ème génération Daclatasvir* Elbasvir ABT-530 Ledipasvir Velpatasvir ACH-3102 Ombitasvir
- 16. Polymérase virale: cibles des molécules
- 18. Adapté de Lindenbach et al. Nature. 2005; 436(7053): 933-8. Inhibiteurs de la polymérase Inhibition de la réplication Liaison au récepteur et endocytose Transport et relargage Réplication ARN Assemblage des virions Traduction et formation de la polyprotéine Fusion et décapsidation ARN (+)
- 19. Inhibiteurs de la Polymérase Nucléosidiques: Analogues de substrats naturels NS5B: très conservée Inhibition compétitive Liaison au site catalytique Tout génotype Haute barrière de résistance Non nucléosidiques Liaison à 1/5 sites allostériques Changement conformationnel du site catalytique Génotype spécifique (1a et 1b) Faible barrière de résistance Sélection de mutants
- 20. Site A Site B Site D Site C Site actif O'Farrell et al. J Mol Biol. 2003; 326(4): 1025-35. Inhibiteurs nucléos(t)idiques de la RdRp* *ARN polymérase ARN dépendante
- 21. SOF 3’ AG C C GA CGGG C 5’ Brin matrice Brin amorce U Les analogues nucléotidiques agissent comme terminateurs de chaine C Blocage de l’élongation de la chaîne d’ARN
- 22. Analogues nucléotidiques Sofosbuvir MK-3682 ACH-3422 AL-335 Activité pangénotypique Forte barrière à la résistance Inhibiteurs nucléos(t)idiques de la RdRp* *ARN polymérase ARN dépendante
- 23. Diminution rapide de la charge virale chez des patients G1 traités par sofosbuvir Lawitz et al. J Viral Hepat. 2013; 20(10): 699-707. Puissance antivirale du sofosbuvir Suivi (jours) ARNVHC(logUI/mL) GS-7977 en monothérapie GS-0938 + GS-7977 À J8 - Diminution significative du taux d’ARN VHC : - 4,65 log (médiane) - 5 patients sur 8 (63 %) avaient un ARN VHC < 15 UI/mL GS-7977 : sofosbuvir GS-0938 : inhibiteur nucléotidique de la polymérase NS5B
- 24. Site A (pouce I) Site B (pouce II) Site D (paume II) Site C (paume I) Site actif Inhibiteurs non-nucléosiques (INN) de la RdRp* *ARN polymérase ARN dépendante O'Farrell et al. J Mol Biol. 2003; 326(4): 1025-35.
- 25. Site A Site B Site C Beclabuvir GS-9669 Dasabuvir Spectre étroit (G1) Faible barrière à la résistance Spectre étroit (G1) Faible barrière à la résistance Spectre étroit (G1) Faible barrière à la résistance Inhibiteurs non-nucléosidiques de la RdRp
- 26. Inhibiteurs de la Polymérase Analogues nucléosidiques: Sofosbuvir (Sovaldi®,Gilead) MK-3682 (MSD) IDX-459 ACH-3422 (Achillion) Inhibiteurs non nucléosidiques Dasabuvir (Exviera®,Abbvie) Becabluvir (BMS) MK-8876 (MSD) TMC-055/r (Janssen)
- 27. Effets indésirables Sans RBV Fatigue Céphalées Insomnie Nausées Toux Dysgueusie Arrêt de trt: <2-3% I Hépatique (Child-Pugh B et C): Viekirax/Exviera®: C.I. Avec RBV Anémie Dyspnée Prurit
- 28. Cas rares d’arythmies cardiaques chez des patients traités par AVD Patient 1 Patient 2 Patient 3 Patient 4 Patient 5 AVD SOF + DCV SOF + DCV + RBV SOF + SMV puis SOF + RBV* SOF + DCV SOF + DCV Amiodarone Non Non Oui Non Non Diagnostic cardiologique Dysfonction sinusale avec échappement jonctionnel FC = 30/mn Tachycardie jonctionnelle FC = 172/mn Dysfonction sinusale FC = 30 /mn syncopale Récidive à la réintroduction BAV 1 avec BAV3 paroxystique syncopal Flutter auriculaire Délai d’apparition J10 J14 J1 puis J6 J6 J5 Pace-maker Oui (J4) Non Oui (J6 de la récidive) Oui (J1) Non Evolution virologique RVS12 RVS12 RVS12 RVS12 Échec * Réintroduction du traitement par AVD Fontaine H, Paris, AASLD 2015, Abs. 1194, actualisé
- 29. Inhibiteurs de la protéine NS5A • Daclatasvir • Ledipasvir • Ombitasvir • ACH-3102 • GSK-805 • Elbasvir (MK-8742) Antiprotéases (anti-NS3/4A) • Boceprevir • Telaprevir • Simeprevir • Asunaprevir • Vaniprevir • Paritaprevir • Grazoprevir (MK-5172) Inhibiteurs de la polymérase NS5B • Sofosbuvir (nucleoside) • MK-382 (nucleoside) • Beclabuvir (INN-1, thumb 1) • Deleobuvir (INN-1, thumb 1) • VX222 (INN-2, thumb 2) • Setrobuvir (INN-3, palm 1) • Dasabuvir (INN-1, palm 1) Position V36 T54 V55 Q80 S122 R155 A156 V158 D168 M175 M28 Q30 L31 H58 Y93 S282 M414 L419 R422 M423 A421 P495 P496 V499 G554 D559 INN: inhibiteur non-nucléosidique Tous les antiviraux directs peuvent sélectionner des variants résistants (2/2)
- 30. Recherche de variants résistants par séquençage chez 312 malades naïfs de génotype 1 Mutations pré-thérapeutiques : NS3 Dietz et al. PLoS One. 2015; 10(8): e0134395. Chez les patients naïfs de traitement, le VHC de génotype 1a serait porteur de mutation de résistance aux anti-NS3 dans environ un tiers des cas Génotype 1a Génotype 1b 59 34,7 % 137 96,5 % WT Q80K WT Q80K Q80K, D168E D168E 111 65,3 % 3 2,1 % 1 0,7 % 1 0,7 %
- 31. Lontok et al. Hepatology. 2015; 62(5): 1623-32. Niveaux de résistance aux antiprotéases (in vitro, système replicon) Fold change par rapport au type sauvage Position RAVs génotype Simeprevir Asunaprevir Paritaprevir Vaniprevir V36 V36M 1a 2 2 V36M+R155K 1a 55 79 V36M+R155K 1b 72 Q80 Q80K 1a 11 3 Q80K+R155K 1a 1830 60 Q80K+R155K 1b 420 Q80R+D168A 1b 2660 R155 R155K 1a 86 21 37 > 1000 A156 A156G 1b 19 16,0 D168 D168A 1a 23 50 D168A 1b 784 127 27
- 32. Mutations pré-thérapeutiques : NS5B Dietz et al. PLoS One. 2015; 10(8): e0134395. Chez les patients naïfs de traitement, le VHC de génotype 1b serait porteur de mutation de résistance aux anti-NS5B dans environ 20% des cas Recherche de variants résistants par séquençage chez 312 malades naïfs de génotype 1 WT C316Y WT C316H C316H, S556G C316N C316Y, Y448H S556G S556N S556R C316N, S556G S556G Génotype 1a Génotype 1b 164 96,5 % 79 55,6 % 32 22,5 % 18 12,7 % 10 7 % 2 1,4 % 1 0,6 % 1 0,6 % 1 0,6 % 1 0,6 % 1 0,6 % 2 2,1 %
- 33. Fold change par rapport au type sauvage Position RAVs Génotype Sofosbuvir (analogue nucléotidique) L159 L159F 3a 1,2 - 1,8 S282 S282T S282T 2a 2b 2 16 V321 V321A 3a 1 Niveaux de résistance au sofosbuvir (in vitro, système replicon) Lontok et al. Hepatology. 2015; 62(5): 1623-32.
- 34. Fold change par rapport au type sauvage Position RAVs Génotype Dasabuvir Beclabuvir C316 C316Y C316Y 1a 1b 1472 1569 M414 M414I M414T 1a 1a 8 32 Y448 Y448H 1a 975 P495 P495A P495L P495 S 1a 1a 1a 12 31 67 A553 A553T 1a 152 G554 G554S 1a 198 S556 S556G S556G 1a 1b 30 11 Niveaux de Résistance aux INN (in vitro, système replicon) Lontok et al. Hepatology. 2015; 62(5): 1623-32. INN : inhibiteurs non-nucléosidiques
- 35. Mutations pré-thérapeutiques : NS5A Génotype 1a Génotype 1b Dietz et al. PLoS One. 2015; 10(8): e0134395. Chez les patients naïfs de traitement, le VHC de génotype 1b serait porteur de mutation de résistance dans environ 20 % des cas Recherche de variants résistants par séquençage chez 312 malades naïfs de génotype 1
- 36. Prévalence des RAVs NS5A détectés en pré-thérapeutique (n=5397 pts, cut-off 1%) Europe 1a: 25% (130/517) 1b: 25% (105/416) Asie Pacifique 1a: 15% (4/27) 1b: 26% (150/570) Océanie 1a: 27% (89/328) 1b: 26% (26/99) Amérique du Nord 1a: 26% (686/2638) 1b: 23% (184/202) USA Canada Porto Rico Belgique Suisse République Tchèque Allemagne Espagne France Royaume Uni Italie Pays-Bas Pologne Chine Inde Japon Corée Russie Taiwan Australie Nouvelle Zélande Avec un cut-off de 15 % (“population sequencing”), la prévalence des RAVs NS5A était de 13 % et 16 % en Amérique du Nord, 14 % et 17 % en Europe, 7 % et 20 % en Asie Pacifique, et 16 % et 19 % en Océanie, pour les génotypes 1a et 1b respectivement
- 37. Fold change par rapport au type sauvage Position RAVs Génotype daclatasvir ledipasvir ombitasvir M28 M28T M28V 1a 1a 205 61 8965 58 Q30 Q30E Q30H Q30R 1a 1a 1a 7500 435 365 5458 183 632 800 L31 L31M L31V L31M L31V 1a 1a 1b 1b 105 1000 3 15 554 H58 H58D 1a 1127 243 Y93 Y93C Y93H Y93N Y93H 1a 1a 1a 1b 555 1600 14 100 12 1602 1677 > 14 706 1675 41 383 66 740 77 Niveaux de résistance aux anti-NS5A (in vitro, système replicon) Lontok et al. Hepatology. 2015; 62(5): 1623-32.
- 38. AASLD 2014 - D’après Sarrazin C et al., abstr. 1926, Polymorphismes NS5A: Impact clinique SOF+LDV+/- RBV SOF+GS-5816+/- RBV GT1 8-Wk Treatment 76% with no NS5A RAVs at baseline: SVR 88% SVR 86% 24% with NS5A RAVs GT2 8-Wk Treatment SVR 81% 51% with NS5A RAVs 49% with no NS5A RAVs at baseline: SVR 94% Tran TT, et al. AASLD 2014. Abstract 80. Taux de réponse plus faible chez les patients de G2 avec RAV La présence de mutations de résistance NS5A avant traitement est peu prédictive d’échec virologique sous SOF/LDV
- 39. Echecs thérapeutiques et résistance Populations Traitement N Échec virologique NS5A RAV lors de l’échec Daclatasvir1 G1/2/3/4 Rx- naïve and -exp. SOF+DCV±RBV 8, 12, 16 ou 24 sem. 616 33 (5.4%) 24 (73%) Ledipasvir2 G1 Rx-naïve and - exp. SOF/LDV±RBV 8, 12 ou 24 sem. 1952 37 (1.9%) 29 (78%) Ombitasvir3 G1/4 Rx-naïve and -exp. G2 Rx-exp. 2D ou 3D±RBV 8, 12 ou 24 sem. 2652 82 (3.1%) 73 (89%) Elbasvir4 G1/4/6 Rx-naïve and -exp. GZR/ELV±RBV 12 sem. 1492 47 (3.1%) 42 (89%) Velpatasvir5 G1/2/3/4/5/6 Rx- naïve and -exp. SOF/VEL±RBV 12 ou 24 sem. 1623 35 (2.1%) 29 (83%) 1) ALLY-2, -3, AI4444040 2) ION-1, -2, -3 3) PEARL-I, -II, -III, -IV, AVIATOR, TURQUOISE-I, SAPPHIRE-II 4) C-SUFFER, C-EDGE, C-SALVAGE, C-WORTHY. 5) ASTRAL-1, -2, -3, -4
- 40. Dvory-Sobol et al. EASL 2015. Abstract O059, actualisé. 98 100 98 100 95 86 0 20 40 60 80 100 VF Baseline FU12 FU24 FU48 FU96 PatientsavecdesRAVNS5A(%) Persistance des variants résistants chez les patients en échec d’un traitement par LDV Les variants NS5A peuvent persister plus de 96 semaines après l’arrêt du traitement chez les patients en échec de traitement à base de NS5A fitness élevé des RAVs NS5A Echec Baseline 12ème semaine de suivi 24 ème semaine de suivi 48 ème semaine de suivi 96 ème semaine de suivi
- 41. Persistance des variants résistants chez des patients GT 1a en échec de traitement 3D Krishnan et al. EASL 2015. Abstract O057, actualisé. Les RAVs NS5A et NS5B sont encore détectables 48 semaines après l’arrêt du traitement *TEV: treatment-emergent resistance-associated variants 46% 9% 0 20 40 60 80 100 PT24W PT48W ProportiondepatientsavecTEV* 97% 96% 0 20 40 60 80 100 PT24W PT48W 75% 57% 0 20 40 60 80 100 PT24W PT48W NS3 NS5A NS5B 24 semaines après l’arrêt du traitement 24 semaines après l’arrêt du traitement 24 semaines après l’arrêt du traitement 48 semaines après l’arrêt du traitement 48 semaines après l’arrêt du traitement 48 semaines après l’arrêt du traitement
- 42. RIBAVIRINE Analogue nucléosidique de la purine Forme active: ribavirine triphosphate Effet anti-viral: Réplication virale: faible ( 0,3 Log) 2 ’5 ’ OAS en synergie avec l ’interféron Inhibition de l ’IMPDH Réduction de synthèse de GTP Mutations possibles (NS5b)
- 43. MECANISME D’ACTION DE LA RIBAVIRINE Glutamine PRA IMP (Inosine monophosphate) XMP (Acide xanthylique) GMP, GDP, GTP Ribavirine Ribavirine - MP
- 45. Les autres molécules … Inhibiteurs Cyclophillines: CPI-431-32 Inhibiteurs ARNmi: Miravirsen RG-101
- 46. ABT-493 (anti-NS3) + ABT-530 (anti-NS5a) 8 semaines chez des patients de G1 (SURVEYOR 1) 34 patients génotype 1 non cirrhotiques Poordad F, Etats-Unis, AASLD 2015, Abs. LB14, actualisé Caractéristiques ABT-493 300 mg + ABT-530 120 mg (n = 34) Homme, n (%) 19 (56) Age, médiane (range), années 54 (28-67) IMC, médiane (range), kg/m² 27 (19-38) G1a, n (%) 24 (71) Génotype IL28B non-CC, n (%) 23 (68) ARN VHC, médiane (range), log10 UI/ml 6,5 (2,9-7,5) ARN VHC > 6 000 000 UI/ml 13 (38) Patients naïfs, n (%) 29 (85) En échec de PR , n (%) 5 (15) Stade initial de fibrose, n (%) F0-F1 24 (70) F2 5 (15) F3 5 (15) 0 20 40 60 80 100 RVS4 RVS12 100 97 34/34 33/34 RVS,patients(%)
- 47. Antiviraux Hépatite B Analogues de: Nucléosides Nucléotides Interféron a Nouvelles cibles Hépatite C Anti-protéases Anti-polymérase: NS5B Nucléosidiques Non nucléosidiques Anti-NS5a Ribavirine Interféron? Inhibiteurs d’entrée Agonistes Toll-like récepteurs
- 48. Les molécules approuvées 1991: Interféron α 1998: Lamivudine 2002: Adéfovir 2005: Peg-Interféron; Entécavir 2006: Telbivudine 2008: Ténofovir
- 50. MOLECULES ANTIVIRALES Analogues de nucléos(t)ides Guanine . Entécavir Adénine . Ara-MP Analogues fluorés . FIAU (Uracyl) Phosphonates de nucléosides acycliques . Adéfovir, Ténofovir Analogues de pyrophosphates . Foscarnet Analogues lévogyres de nucléosides . Lamivudine (Cytidine) . FTC ou Emtricitabine (Cytidine) . L-dT (Telbivudine) . LFD4C (Cytidine)
- 51. ANALOGUES DE NUCLEOSIDES Efficacité Bonne captation cellulaire Phosphorylation par les kinases cellulaires (tri- phosphate) Degré de compétition avec les nucléosides naturels endo-cellulaires Efficacité de la liaison à la polymérase virale et de son incorporation dans la chaine d ’ADN naissante
- 53. TRANSLOCATION et ELONGATION Lamivudine Emtricitabine Entécavir 3 ’ AAA POL 5 ’ AATG DR1 Adéfovir Ténofovir
- 54. ENTECAVIR Analogue de la guanine Inhibiteur sélectif et puissant du VHB (EC50 = 4 nM, Ki = 1 nM) Agit à 3 niveaux de la polymérase: Initiation Synthèse ADN-dépendante Reverse transcription N NH N N OH OH O CH2 NH2
- 55. 0 0,5 1 1,5 2 2,5 3 3,5 0 1 2 3 4 6 8 Placebo 0.05 mg 0.1 mg 0.5 mg 1.0 mg Dosing Weeks ENTECAVIR :ADN VHB
- 56. TENOFOVIR Analogue nucléotidique (monophosphorylé) Utilisé dans le VIH depuis 2000 Inhibe l’ADN Polymérase Terminateur de chaine Plus efficace que l’Adéfovir Aucune mutation de résistance à 6 ans Tolérance rénale bonne mais: Clairance à surveiller Hypophosphorémie
- 57. Réduction de l’ADN du VHB après 1 an de Traitement -8 -7 -6 -5 -4 -3 -2 -1 0 ADV1 10 mg ADV2 30 mg LAM3 LdT3 ETV4 TDF5 -3,5 -4,8 -5,5 -6,5 -6,9 -6,4 *Données issues d’études indépendantes, ne permettant pas de comparaisons (populations différentes, valeurs initiales de charges virales et méthodes de quantifications de l’ADN du VHB différentes) Patients AgHBe-positifs 1Hepsera [RCP]; 2Marcellin et al., N Engl J Med 2003, 348: 808-16; 3Sebivio [RCP]; 4Baraclude [RCP]. 5Heathcote et al., AASLD 2007, abstract LB6; Fontana R.J., Gastroenterlogy 2009, 136(2):389-92. Réductiondel’ADNduVHB à1an(Log10)
- 58. 845 a.a. Terminal protein spacer Pol/RT RNaseH A B C ED 1 183 349 692 YMDD V173L L180M M204I/V GVGLSPFLLA I(G) II(F) (rt1) (rt 344) MUTATIONS DE RESISTANCE LAM / FTC ETV T184G S202I M250V ADV A181V N236T LdT M204I Allen Hepatology 1998, Delaney J Virol 2003, Angus Gastroenterology 2003, Villeneuve J Hepatol 2003, Lai AASLD 2003, Colonno HepDart 2003
- 59. LVD1 ETV*5,6 LdT†2,3 ADV‡1 TDF§4 Résistance à 6 ans § Patients avec ADN VHB ≥400 copies/mL à S72 peuvent ajouter FTC au TDF; ainsi la résistanceau TDF monotherapie après 72 semaines ne peut pas être totallement certifiée5,6 * probabilité cumulée d’apparition de résistance; † AgHBe (+) naïf; ‡ AgHBe(-) Naïf; N/A non disponible Année 3 1.2% 0% 55% 11% Année 4 1.2% – 0% 71% 18% Année 2 <1% 0%§ 46% 3% 25% Année 1 <1% 0% 23% 0% 5% Année 5 – 0% 80% 29% 1.2% Année 6 0% – – – 72 SEMAINES 1. Locarnini S. Hepatol Int. 2008;2:147-51. 2. Lai CL, et al. N Engl J Med, 2007;357:2576-8; 3. Liaw YF, et al. Gastroenterology 2009;136:486-95. 4. Snow-Lampart A, et al. AASLD Oct 31–Nov 4, 2008, San Francisco, USA. Oral Presentation 977 Hepatology 2008;48:745A. 5. Baraclude EU SmPC, February 2009. 6. Tenney et al. EASL April 22–26, 2009, Copenhagen, Denmark, Oral – 1.2%
- 60. TOLERANCE Rash Tenofovir Adefovir Lamivudine Telbivudine Entecavir Amylase,lipase Peripheral neuropathy Myalgia, rhabdomyolyse CPK Pancreatite Nécrose tubulaire ClCréatinine Hypophosph atemie Acidose lactique Thrombocyto penie Dyspnée Malaise Céphalées Gastrointesti nal Vertige Très fréquent: 1/10 Rare: 1/1,000-1/10,000 fréquent: 1/100-1/1,000 Très rare: >1/10,000 Expert Panel Italian Guidelines STI review 2009;2:14-27.
- 61. Tenofovir alafénamide Prodrogue Réduit la concentration sanguine Limite les effets II: osseux et rénaux DMO hanches et vertèbres DFG amélioré Demande d’autorisation: mars 2016? 64 94 67 93 Ag Hbe(+) Ag Hbe(-) ADN VHB (-) à S48 TAF TDF
- 62. INTERFERONS . Protéines ou glycoprotéines . Spécifiques de l’espèce . Agissant sur la cellule cible (récepteur) . Expression de certains gènes : synthèse des ARNm et protéines
- 63. INTERFERON Action des principales enzymes induites : 1°) 2’ 5’ oligoadénylate synthétase : - catalyse synthèse d’oligomères d’adénine - oligomères activent endonucléase - destruction des ARN viraux 2°) Protéine kinase P1 - Sérine thréonine kinase - initiation de la synthèse protéique
- 64. INTERFERON ALPHA Effet immunomodulateur IFN IFN IFN IFN HLA II Th0 Th2 Activation Cellule B Prolifération Anticorps IFN Activation IL12 rIL12 Th1 CTL NK HLA I
- 65. CHARACTERISTIQUES DES IFN-PEG Taille: 40kDa Structure: branché Dose fixe Clairance hépatique Taille: 12kDa Structure: linéaire Dose adaptée au poids Clairance rénale PEG-IFN 2a PEG-IFN 2b
- 66. Les nouvelles thérapeutiques Anti-viraux directs Approuvés: Inhibiteurs de polymérase Potentiels: Prodrogues de I.P. Inhibiteurs de l’AgHBs Inhibiteurs de capside Inhibiteurs de Rnase-H CRISPR/Cas9 système ciblant le cccDNA Inhibiteurs d’attachement Anti-viraux ciblant l’hôte Immunomodulateurs: Approuvé: Interféron Potentiels: Agonistes TLR Vaccins Cytokines, Interleukines Fonction de l’hôte: Approuvé:0 Potentiels: Inhibiteurs d’entrée Modificateurs épigénétiques
- 67. Les molécules en développement
- 68. Les molécules en développement
Notes de l'éditeur
- Le cycle viral du virus de l’hépatite C (VHC) comprend classiquement 3 étapes majeures: 1- Les étapes précoces correspondant à l’adsorption des particules virales à la surface des hépatocytes via l’interaction avec un complexe récepteur (HS, CD81, SRB-I, occludin et claudin-1, etc). Il s’ensuit un internalisation de la particule virale dans une vésicule d’endocytose qui après acidification va permettre la libération de la nucléocapside dans le cytoplasme. L’ARN de polarité positive va être pris en charge par les ribosomes cytosoliques. La traduction permettant ainsi la synthèse de la polyprotéine qui va subir une maturation co- et post-traductionnelle afin de générer les différentes protéines structurales (C, E1, E2) et non structurales (p7, NS2, NS3/4A, NS4B, NS5A, NS5B). 2- la réplication du génome viral au sein des complexes des réplication (« membranous web ») en association très étroite avec les membranes du RE et des protéines cellulaires (CYPA, PI4KIIIalpha, etc…). De nombreux copies identiques à la molécule parentale sont ainsi synthétisées 3- Les étapes tardives correspondant à la formation des nouvelles particules virales et leur maturation avec en particulier la glycosylation des protéines d’enveloppe E1 et E2. Les antiviraux directs (antiprotéases, anti-NS5A et anti-NS5B) sont capables de bloquer une ou plusieurs étapes du cycle viral aboutissant à une diminution drastique da la quantité de particules virales circulantes (diminution de la charge virale) Lindenbach BD, Rice CM. Unravelling hepatitis C virus replication from genome to function. Nature. 2005; 436(7053): 933-8.
- Lindenbach BD, Rice CM. Unravelling hepatitis C virus replication from genome to function. Nature. 2005; 436(7053): 933-8.
- Saalau-Bethell SM, Woodhead AJ, Chessari G, Carr MG, Coyle J, Graham B et al. Discovery of an allosteric mechanism for the regulation of HCV NS3 protein function. Nat Chem Biol. 2012; 8(11): 920-5.
- Tellinghuisen TL, Marcotrigiano J, Rice CM. Structure of the zinc-binding domain of an essential component of the hepatitis C virus replicase. Nature. 2005; 435(7040): 374-9.
- Les anti-NS5A (représenté en bleu-vert) lie le dimère NS5A-NS5A à la membrane du RE (réticulum endoplasmique) en interagissant avec les résidus Y93 des 2 molécules A et B (A-Y93-B). Les résidus en position 31 (L31) sont également impliqués dans cette interaction. Nettles JH, Stanton RA, Broyde J, Amblard F, Zhang H, Zhou L et al. Asymmetric binding to NS5A by daclatasvir (BMS-790052) and analogs suggests two novel modes of HCV inhibition. J Med Chem. 2014; 57(23): 10031-43.
- Plusieurs mécanismes d’action des anti-NS5A ont été décrits dans la littérature: 1-Inhibition de la formation des complexes de réplication 2- Inhibition du recrutement de la protéine kinase PI4KIII alpha 3- Augmentation de la stabilité de la protéine NS5A 4-Augmentation de la capacité de dimérisation de NS5A 5-Facilitation de la disruption des complexes NS5A Eyre NS, Beard MR. HCV NS5A inhibitors disrupt replication factory formation: a novel mechanism of antiviral action. Gastroenterology. 2014; 147(5): 959-62.
- Lindenbach BD, Rice CM. Unravelling hepatitis C virus replication from genome to function. Nature. 2005; 436(7053): 933-8.
- RdRp: RNA-dependent RNA polymerase Sites A, B, C et D : sites allostériques O'Farrell D, Trowbridge R, Rowlands D, Jäger J. Substrate complexes of hepatitis C virus RNA polymerase (HC-J4): structural evidence for nucleotide import and de-novo initiation. J Mol Biol. 2003; 326(4): 1025-35.
- SOF : sofosbuvir
- 48 patients au total 8 dans la cohorte 3 Lawitz EJ, Rodriguez-Torres M, Denning J, Mathias A, Mo H, Gao B et al. All-oral therapy with nucleotide inhibitors sofosbuvir and GS-0938 for 14 days in treatment-naive genotype 1 hepatitis C (NUCLEAR). J Viral Hepat. 2013; 20(10): 699-707.
- O'Farrell D, Trowbridge R, Rowlands D, Jäger J. Substrate complexes of hepatitis C virus RNA polymerase (HC-J4): structural evidence for nucleotide import and de-novo initiation. J Mol Biol. 2003; 326(4): 1025-35.
- Dietz J, Susser S, Berkowski C, Perner D, Zeuzem S, Sarrazin C. Consideration of Viral Resistance for Optimization of Direct Antiviral Therapy of Hepatitis C Virus Genotype 1-Infected Patients. PLoS One. 2015; 10(8): e0134395.
- Lontok E, Harrington P, Howe A, Kieffer T, Lennerstrand J, Lenz O et al. Hepatitis C virus drug resistance-associated substitutions: State of the art summary. Hepatology. 2015; 62(5): 1623-32.
- Dietz J, Susser S, Berkowski C, Perner D, Zeuzem S, Sarrazin C. Consideration of Viral Resistance for Optimization of Direct Antiviral Therapy of Hepatitis C Virus Genotype 1-Infected Patients. PLoS One. 2015; 10(8): e0134395
- Lontok E, Harrington P, Howe A, Kieffer T, Lennerstrand J, Lenz O et al. Hepatitis C virus drug resistance-associated substitutions: State of the art summary. Hepatology. 2015; 62(5): 1623-32.
- Lontok E, Harrington P, Howe A, Kieffer T, Lennerstrand J, Lenz O et al. Hepatitis C virus drug resistance-associated substitutions: State of the art summary. Hepatology. 2015; 62(5): 1623-32.
- Dietz J, Susser S, Berkowski C, Perner D, Zeuzem S, Sarrazin C. Consideration of Viral Resistance for Optimization of Direct Antiviral Therapy of Hepatitis C Virus Genotype 1-Infected Patients. PLoS One. 2015; 10(8): e0134395.
- AASLD 2015 – D’après Zeuzem S, Mizokami M, Pianko S, Mangia A, Han KH, Martin R et al. Prevalence of Pre-Treatment NS5A Resistance Associated Variants in Genotype 1 Patients Across Different Regions Using Deep Sequencing and Effect on Treatment Outcome with LDV/SOF. Abtract 91.
- Lontok E, Harrington P, Howe A, Kieffer T, Lennerstrand J, Lenz O et al. Hepatitis C virus drug resistance-associated substitutions: State of the art summary. Hepatology. 2015; 62(5): 1623-32.
- Traduction dans les essais cliniques: Sur GT1a impact un peu plus important des mutations que sur 1b GS-5816, a Second-Generation HCV NS5A Inhibitor With Potent Antiviral Activity, Broad Genotypic Coverage, and a High Resistance Barrier EC50 augmente dans G2 si M en position 31 Ppx polymorphisms chez G1= L31M, Y93C/H et L31M chez >50% des G2, A30K in GT3
- 1) ALLY-2, -3, AI4444040 2) ION-1, -2, -3 3) PEARL-I, -II, -III, -IV, AVIATOR, TURQUOISE-I, SAPPHIRE-II 4) C-SUFFER, C-EDGE, C-SALVAGE, C-WORTHY 5) ASTRAL-1, -2, -3, -4
- EASL 2015 – D’après Dvory-Sobol H, Wyles D, Ouyang W, Chodavarapu K, McNally J, Cheng W et al. Long-term persistence of HCV NS5A variants after treatment with NS5A inhibitor ledipasvir. Abstract O059, actualisé.
- Du fait des taux de RVS élevés, la persistance des variants viraux n’a été évaluée que chez les patients de génotype 1a Plus de 3 500 patients GT 1 inclus dans l’étude, 93 (2,6 %) n’ont pas eu de RVS 85 patients GT 1a 8 patients GT 1b Suivi pendant 48 semaines Les variants de résistance ont été détectés par des analyses de séquençage de population ou de clonage-séquençage EASL 2015 – D’après Krishnan P, Tripathi R, Schnell G, Reisch T, Beyer J, Dekhtar T et al. Long-term follow-up of treatment emergent resistance-associated variants in NS3, NS5A and NS5B with paritaprevir/r-, ombitasvir- and dasabuvir-based regimens. Abstract O057, actualisé.
- ABT-493 : inhibiteur NS3/4a pangénotypique. ABT-530 : inhibiteur NS5a pangénotypique. Cette étude de phase IIb est la suite de l’étude SURVEYOR-1 et confirme que cette nouvelle association pangénotypique très puissante permet d’envisager des traitements courts avec une bonne tolérance chez les patients de génotype 1.